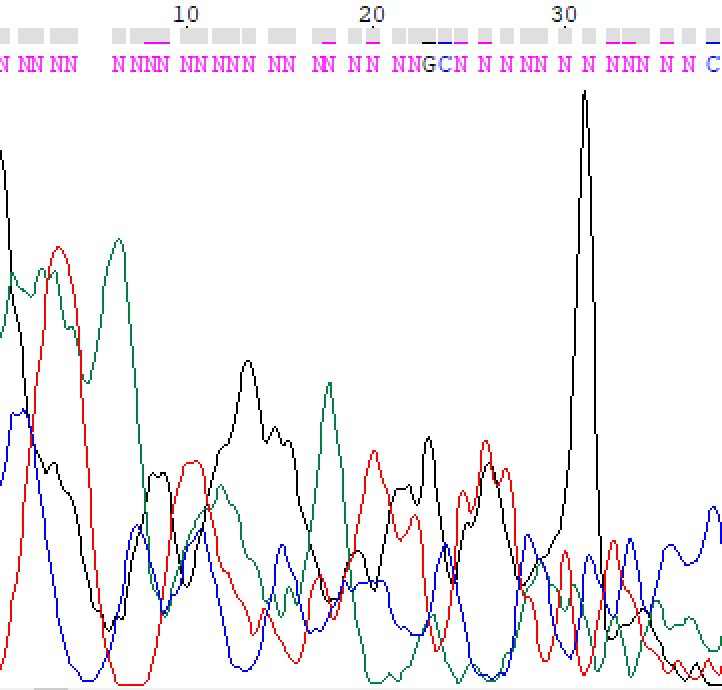
В этом практикуме мне были даны файла с хроматограммами прямой и обратной последовательностей ДНК.
Для анализа хроматограмм я использовала программу Chromas, тк с GeneStudio возникли проблемы.
Сначала я открыла прямую и обратную послдеовательности в двух разных вкладках. Затем обратную последовательность сделала комплементарной с помощью Reverse. Выравнание хроматограмм было сделано вручную. Файл с выравниванием последовательностей в BLAST представлен ниже.
Были найдены(см таблицу ниже), а затем удалены нечитаемые концы.
| Границы нечитаемых 5'- и 3'-участков | 5'-участок | 3'-участок |
| Прямая последовательность | 1 -23 | 375-377 |
| Обратная последовательность | 1-29 | - |
Общий вид хроматограмм я могу назвать достаточно неплохим, в обратной последовательности даже нет нечитаемого участка на одном из концов. Уровень шума на обоих хроматограммах схожий. Ярко выраженные пики встречатся примерно через 15-25 нуклеотдиов. Уровень сигнала в 2-2.5 раза выше уровня шума.
Сложных участков на данных хроматограммах оказалось не так много.
Не определены несколько проблемных нуклеотидов из-за уровня шума выше среднего. Обратной последовательности в этих участках нет, так что не получается понять что там за нуклеотиды.

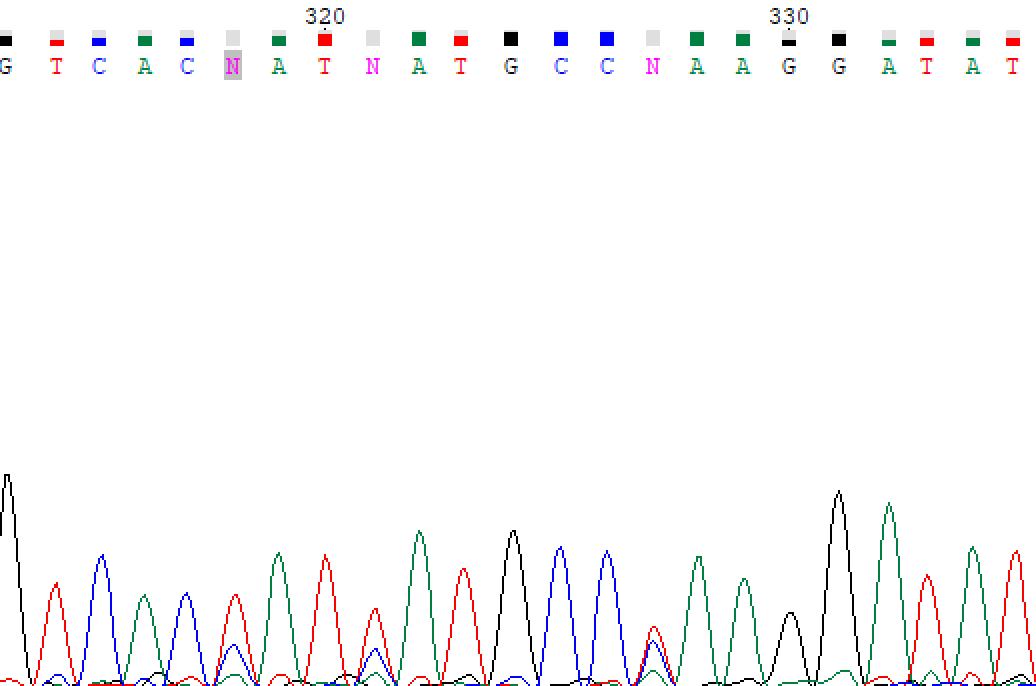
Неопределнный нуклеотид прямой последовательности сразу после нечитаемого конца. На обратной последовательности чётко видим что там гуанин.
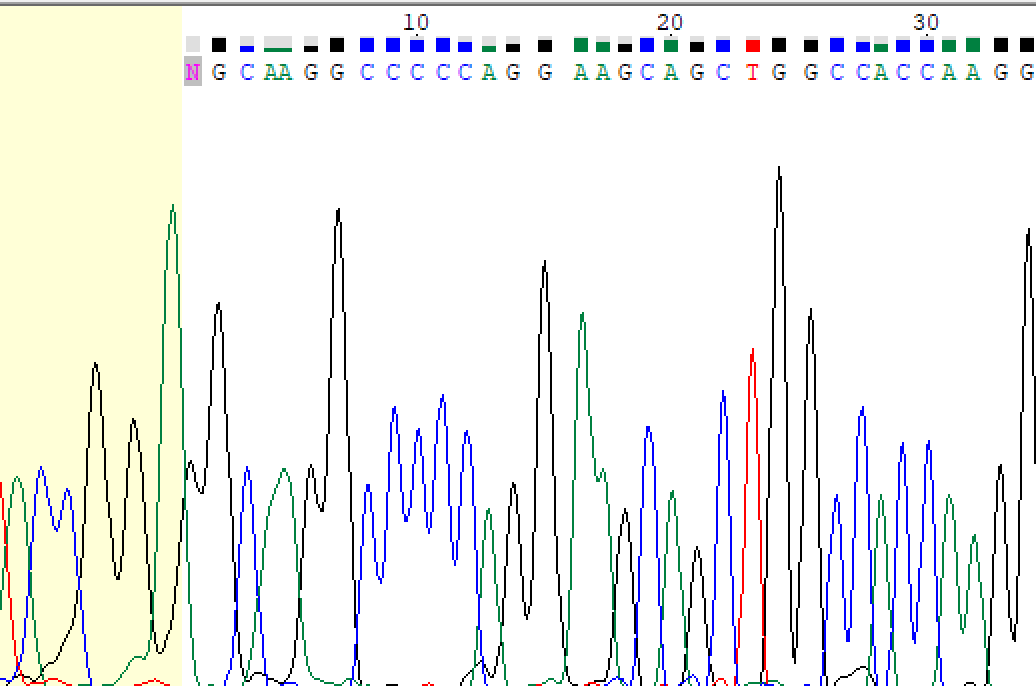
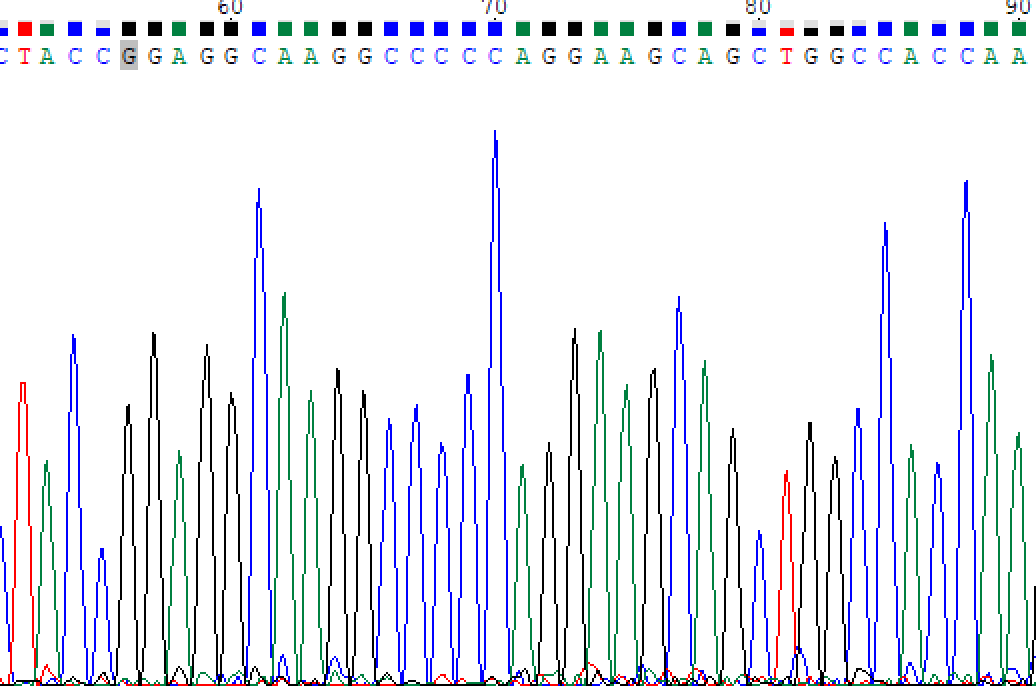
Тут с определением нуклеотидов все нормально, но пики слились в один большой, причем это участок обратной последовательности.
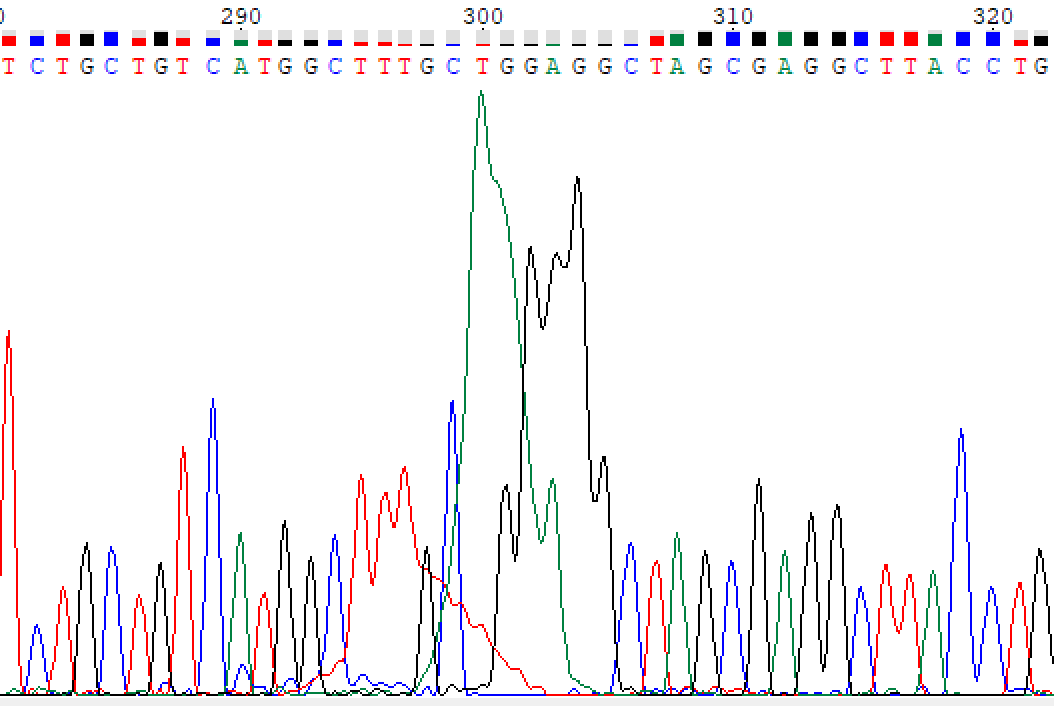
Я взяла плохую хромотограмму в папке bad. На картинке ниже ее участок.Видим, что хромтаграмму прочитать нереально, тк сигналы смешаны друг с другом. Можно предположить, что такое произошло из-за того, что в препарате нахоидлись две матрицы ДНК.